La resistencia a los antimicrobianos es un problema grave para la salud pública a nivel global, cuya abundancia, diversidad y distribución espacial es dificil de conocer. Analizar las aguas residuales no sólo puede aportar información sobre la presencia y distribución de microorganismos patógenos en zonas geográficas determinadas, sino también monitorizar e incluso predecir la aparición de resistencias antimicrobianas entre ellos.
Analizar el material genético de las aguas residuales es una fuente de información rápida, exacta y económica sobre los tipos y niveles de bacterias resistentes a los agentes antimicrobianos. Asi lo muestra un estudio internacional, dirigido por la Technical University of Denmark, en el que ha participado el Institut de Recerca i Tecnologia Alimentàries (IRTA).
A partir del análisis metagenómico de aguas residuales sin tratar de 74 ciudades de 60 países diferentes, en el estudio se caracteriza la abundancia y la diversidad de resistencia antimicrobiana (RAM) en diversas zonas del planeta. Estos se consideran los primeros datos globales comparables de los niveles y los tipos de bacterias resistentes a los antibióticos que hay a nivel mundial.
Mediante el análisis del ADN de las muestras, se ha podido identificar un abanico muy amplio de genes que confieren resistencia a antibióticos y, según los resultados, existen diferencias sistemáticas en la abundancia y diversidad de estos genes entre dos grupos de regiones. América del Norte, Europa occidental, Australia y Nueva Zelanda es la zona donde hay un nivel más bajo de resistencia antimicrobiana. Por otra parte, Asia, África y América del Sur presentan un nivel mucho más alto.
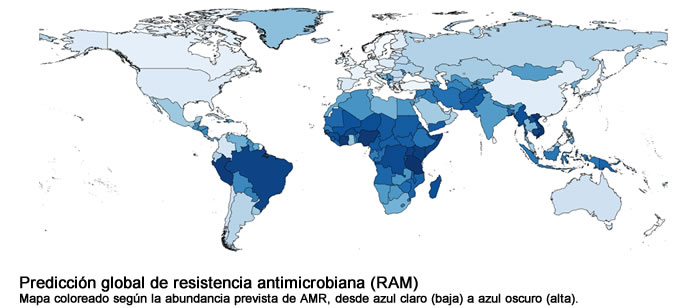
Brasil, India y Vietnam son los paises donde se ha encontrado más diversidad de genes de resistencia en las aguas residuales analizadas, lo que, según Marta Cerdà, investigadora del IRTA-CReSA, sugiere que estos países podrían ser puntos calientes de emergencia de nuevos mecanismos de resistencia a los antibióticos.
Factores socioeconómicos y de salud
El uso que hace de los antimicrobianos la población de un país sólo explican una parte de las variaciones de resistencia observadas. En cambio, los autores del estudio detectaron una fuerte correlación entre la abundancia de genes de resistencia y factores socioeconómicos y de salud de la población.
Dado que los viajes aéreos humanos no tuvieron una influencia significativa en la abundancia de la RAM, es importante destacar que esto sugiere que la abundancia total de RAM está influenciada principalmente por los parámetros locales / nacionales, y aunque los genes de RAM podrían diseminarse rápidamente y encontrarse en todos los rincones del mundo, se requiere la selección local para que alcancen frecuencias apreciables.
Estos hallazgos sugieren que seria muy efectivo mejorar el saneamiento, la salud y quizás la educación en los países en que hay niveles más altos de resistencia antimicrobiana, para hacer frente a este problema global.
Vigilancia global a través de las aguas residuales
Analizar las aguas residuales permite determinar de forma rápida, precisa y relativamente económica qué bacterias hay en un área geográfica determinada.
Los autores del estudio proponen el análisis metagenómico de las aguas residuales como un enfoque éticamente aceptable, ya que se trata de un tipo de muestra que no se puede rastrear a nivel de individuo, y económicamente viable, para establecer un sistema de vigilancia y predicción global continua de la resistencia a los antimicrobianos.Esta información permitiría gestionar la presencia y la distribución de microorganismos que provocan enfermedades, así como de resistencias antimicrobianas, más allá de las fronteras de un país.
Fuente: IRTA
Artículo de referencia: Hendriksen et al. (2019). Global monitoring of antimicrobial resistance based on metagenomics analyses of urban sewage. Nature Communications. 10:1124. DOI: 10.1038/s41467-019-08853-3